基因注释是连接“测出基因组”和“读懂基因组”的核心环节,是基因组研究走向功能解析和应用转化的重要基础。随着国际大型基因组计划持续产出海量数据,如何实现高质量基因注释已成为后基因组时代亟待突破的重要瓶颈。传统方法通常依赖RNA测序、同源蛋白等外部证据,存在数据需求高、计算开销大、对数据匮乏物种适用性受限等问题。
针对这一挑战,西安交通大学叶凯教授团队提出了一种基于混合专家架构的基因组语言模型ANNEVO(图1)。该方法能够同时学习不同生物类群的进化规律和长距离序列上下文关系,在无需RNA测序和同源蛋白等外部证据的条件下,仅凭DNA序列即可实现高精度从头基因注释,打破国外尤其是德国团队在该领域二十余年的技术垄断,推动我国在基因注释核心方法上实现重要突破,对于服务国家生物安全战略、AI+生命交叉融合发展具有重要意义。相关成果以《使用ANNEVO进行高精度从头基因注释》为题,于2026年3月12日在线发表于国际顶级期刊《自然·方法》。
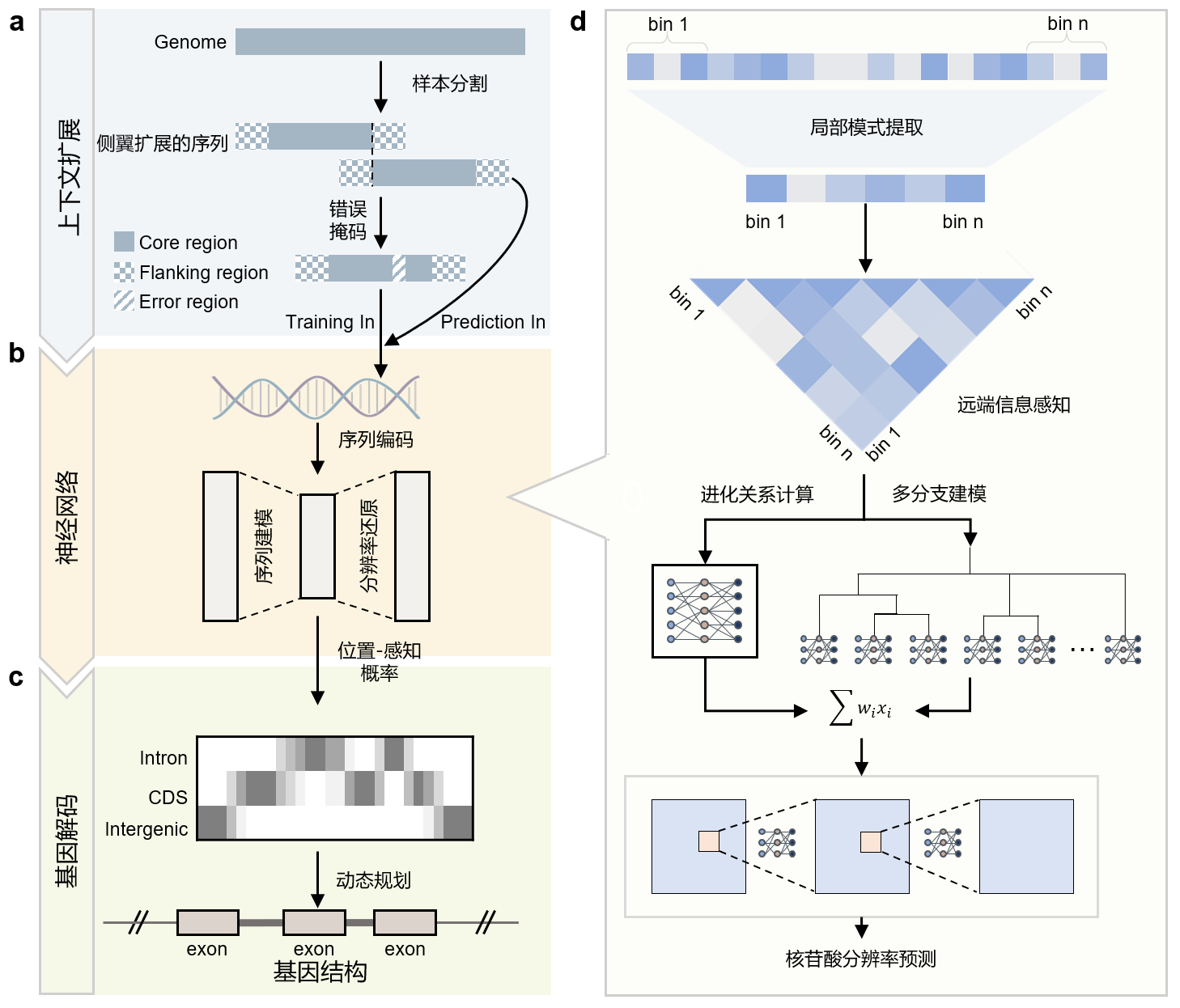
图1. ANNEVO方法概览
研究团队长期围绕“人工智能驱动基因组解析”开展系统布局,此前已相继提出SVision(《自然·方法》,2022)、SVision-pro(《自然·生物技术》,2024)和Swave(《自然·遗传》,2026)等方法。此次ANNEVO的提出,进一步完善了团队在“AI驱动基因组解析”方向上的系列工作布局(图2),形成了从基因组变异识别到基因功能注释的连续方法链条,已在Darwin Tree of Life等国际旗舰基因组计划场景中展现出重要应用价值。
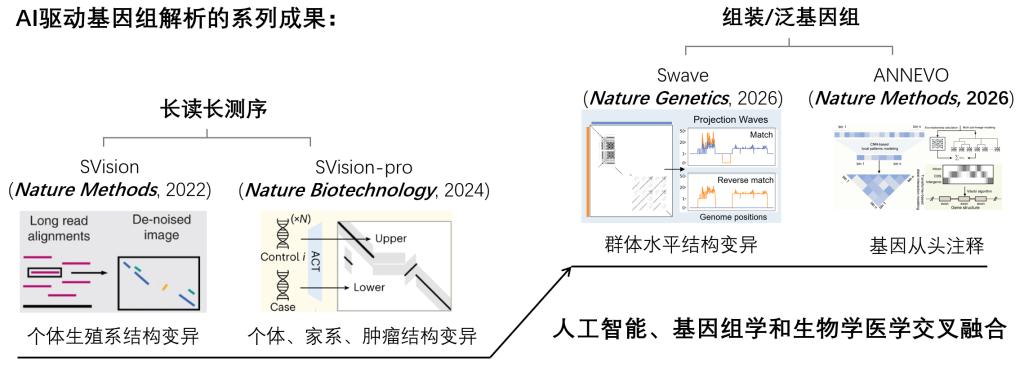
图2. 团队系列成果概览
西安交通大学即将迎来建校130周年暨西迁70周年,此次成果的发布,也恰逢叶凯教授到校开展工作十年,具有重要意义。这一成果既是团队十年深耕“人工智能+基因组”交叉前沿的重要阶段性总结,也是学校持续加强基础研究、推动学科交叉、服务国家重大需求的生动体现。研究过程中,团队与数学学院孟德宇教授团队开展密切合作,体现了学校推动学科交叉融合的良好成效;西安交通大学“珠峰计划”本科生张奕哲积极参与相关研究,展现了学校在拔尖创新人才培养方面的积极探索。该成果也是学校持续推进“人工智能+生命医学”交叉融合的重要进展。
电信学部自动化学院博士生张鹏宇为该论文第一作者,叶凯教授为通讯作者。本论文受到了科技部重点研发专项、国家杰出青年科学基金和国家自然科学基金委重点项目等项目资助。
西安交通大学信息与生物医学交叉研究中心团队主页:https://gr.xjtu.edu.cn/en/web/kaiye
论文链接:https://www.nature.com/articles/s41592-026-03036-7