近日,西安交通大学叶凯教授团队在《自然·遗传学》发表研究论文,提出面向泛基因组图的人群水平结构变异(SV)解析新方法Swave。该工作聚焦“群体结构变异检测和分型”的关键难题,为群体复杂结构变异图谱的刻画提供了新工具,是叶凯教授团队在人工智能与生命医学交叉领域取得的又一项创新成果。
基因组变异是疾病发生发展、物种形成演化等生物学核心过程的重要驱动力。尽管基因组组装和泛基因组技术的快速发展使群体尺度结构变异分析成为可能,但复杂变异识别难、重复区域噪声干扰强、跨样本分析基因型缺失率高等问题,仍是该领域长期存在的重要瓶颈。如何在大规模人群数据中更准确地发现并解构复杂结构变异,已成为基因组学研究和医学应用共同关注的关键问题。
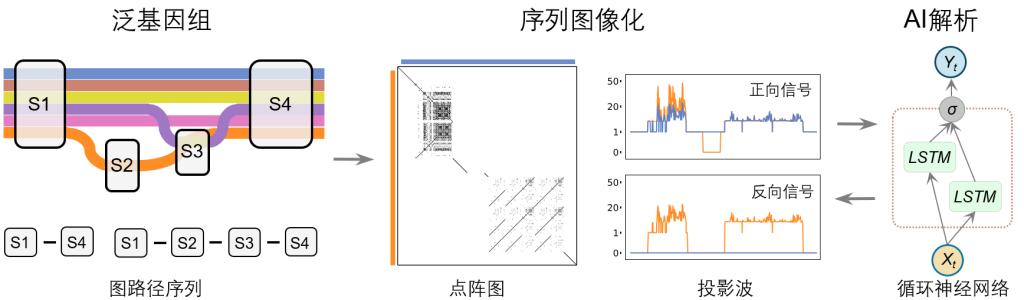
图1.Swave方法概览
针对上述难题,叶凯教授团队提出的Swave方法(如图1),通过“点阵图投影波”的策略对序列进行升维、去噪和特征提取,进而结合AI循环神经网络,自动化地进行变异类型判别和样本分型。Swave在结构变异识别准确性、家系一致性以及群体基因型完整性等指标上优于现有方法。团队进一步将该方法应用于健康人群和罕见病队列的泛基因组分析,发现复杂结构变异中存在大量此前容易被低估的稀有低频事件,并提示其在致病机制、演化机制研究中的重要价值。
叶凯教授团队这一研究体现了人工智能在生命信息复杂模式识别中的独特优势,也展示了计算方法创新对生物学、医学问题研究的重要支撑作用。值得关注的是,该成果与团队此前的个体结构变异检测(SVision,《自然·方法》,2022)、跨样本结构变异比较(SVision-pro, 《自然·生物技术》,2024)以及近期发表的高精度基因注释(ANNEVO) 共同构成“AI驱动基因组解析”的系列布局,体现了团队在人工智能方法、基因组学关键问题和生物学医学应用场景之间持续打通的能力。
西安交通大学即将迎来建校130周年暨西迁70周年,此次成果的发布,也恰逢叶凯教授到校开展工作十年,具有重要意义。该成果面向国家战略需求和人民生命健康,依托西安交通大学在人工智能、自动化、数学、计算机与生命医学等方向的交叉布局,以及西安交通大学第一附属医院在临床资源、医学问题牵引和转化平台建设方面的支撑,是持续推进“人工智能+生命医学”交叉融合、服务高水平科技自立自强的代表性进展之一。
西安交通大学自动化学院王松渤助理教授为该论文第一作者、叶凯教授为通讯作者。本论文受到了科技部重点研发专项以及国家自然科学基金委国家杰出青年科学基金、重点项目、青年学生基础研究项目(博士研究生)等项目资助。
西安交通大学信息与生物医学交叉研究中心团队主页:https://gr.xjtu.edu.cn/en/web/kaiye
论文链接:https://www.nature.com/articles/s41588-026-02538-6